摘要
本研究对海水(SEA)与淡水(TAP)环境下鳗鲡的三个关键组织(脑部、性腺、胸鳍)进行了差异表达基因(DEG)分析,旨在揭示鳗鲡在盐度适应过程中的转录组响应机制。
主要发现:
- 全局分析(控制组织效应)鉴定出 422 个 DEG(303 上调,119 下调)
- 脑部对盐度变化最为敏感,共鉴定出 500 个 DEG
- 三组织共同显著(交集)的核心响应基因共 8 个,全部在海水环境中上调表达
主要结论:
- 日本鳗鲡对盐度变化具有组织特异性的转录组响应,其中脑部响应最强,胸鳍最保守。
- 海水环境激活了更多基因(全局分析:72% 上调),表明海水盐度环境促进了特定的基因表达程序。
- 不同组织的响应模式差异反映了组织特异性功能对环境盐度的差异化适应策略。
一、材料与方法
1.1 样本信息
实验选用的是2017年5月31日在泉州地区购买的非野生养殖鳗。购买时,挑选体重300g - 1000g,体型较鼓,胸鳍圆钝、颜色深,背黑腹银的鳗鲡。此为下海前雌性银鳗的典型特征,形态学上雌雄鉴别的准确率约为90%1。
从5条非野生鳗中随机挑选3条进行盐度驯化,与淡水养殖的鳗鲡形成对照。每日定时添加6.6‰海水盐,到第五天,实验组鳗鲡所处环境达到30‰左右的盐浓度(海水盐度约为35‰),模拟日本鳗鲡洄游入海的盐度变化过程。
取样时,将全部5条日本鳗鲡经冰水处理达到麻痹的效果,之后可进行形态指标的测量及解剖。每条日本鳗鲡各取脑部、性腺及胸鳍作为RNA测序样本,为避免RNA水解,取下后立即投入液态氮中冷冻保护。
| 样本 | 体长(mm) | 体重(g) | 水平眼径(mm) | 垂直眼径(mm) | 眼间距(mm) | 吻长(mm) | 胸鳍长(mm) | 胸鳍宽(mm) | 肛门到腹鳍起始端(mm) |
|---|---|---|---|---|---|---|---|---|---|
| SEA_1 | 695 | 553 | 12 | 11 | 15 | 12 | 35 | 16 | 5 |
| SEA_2 | 650 | 570 | 10 | 9 | 13 | 13 | 30 | 20 | 4 |
| SEA_3 | 680 | 600 | 11 | 11 | 13 | 13 | 30 | 16 | 4 |
| TAP_1 | 675 | 610 | / | / | / | / | 30 | 20 | 8 |
| TAP_2 | 715 | 650 | 9 | 10 | 15 | 16 | 27 | 18 | 5 |
注:
- SEA_N:实验组,TAP_N:对照组;
- 体长:吻端至尾鳍基部的长度;
- 水平眼径:眼眶前缘至后缘的宽度;垂直眼径:眼眶上缘至下缘的宽度;
- 眼间距:两眼中心之间的宽度;
- 吻长:眼眶前缘至吻尖的长度;
- 胸鳍长:胸鳍基部至末端的长度。
本分析共包含 15 个样本,涵盖 3 种组织和 2 种盐度处理条件:
| 组织 | 海水组(SEA) | 淡水组(TAP) |
|---|---|---|
| 脑部(brain) | BR_SEA_1, BR_SEA_2, BR_SEA_3 | BR_TAP_1, BR_TAP_2 |
| 性腺(gonad) | GD_SEA_1, GD_SEA_2, GD_SEA_3 | GD_TAP_1, GD_TAP_2 |
| 胸鳍(pectoral fins) | PF_SEA_1, PF_SEA_2, PF_SEA_3 | PF_TAP_1, PF_TAP_2 |
1.2 数据预处理
本分析基于转录组测序数据,通过无参 Trinity 拼接获得 16,920 个假定基因。为降低测序深度对分析结果的影响,我们对基因表达量进行了过滤,剔除在至少 3 个样本中 counts 值低于 10 的基因,最终保留 16,866 个基因用于后续差异表达分析。
1.3 统计分析方法
本分析采用两种设计策略(显著性阈值:padj < 0.05):
| 特征 | 全局分析 (控制组织效应) | 各组织单独分析 |
|---|---|---|
| 设计公式 | ~tissue + treatment |
~treatment |
| 样本范围 | 全部 15 个样本 | 每个组织 5 个样本 |
| metadata | 包含 tissue 和 treatment |
仅包含 treatment |
| 目的 | 检测跨组织一致的处理效应 | 检测特定组织内的处理效应 |
全局分析(多因素模型)
design = ~tissue + treatment
全局分析使用多因素线性模型,控制组织间基线差异,检测跨组织一致的处理效应:
$$ log2(μ_ij) = β_0 + β_{tissue_j} + β_{treatment} · X_{treatment} $$其中:
- $β_0$:截距(基准表达水平)
- $β_{tissue_j}$:组织效应 — 不同组织(脑、性腺、胸鳍)之间的基线表达差异
- $β_{treatment}$:处理效应 — 在控制组织差异后,SEA vs TAP 的表达变化
将组织作为协变量(covariate)加入模型表示:
- 模型先"扣除"掉不同组织本身的基础表达差异
- 然后估计一个统一的 treatment 效应(适用于所有组织)
- 假设处理效应在不同组织中是相同的
各组织单独分析(单因素模型)
design = ~treatment
在每个组织内独立检测海水 vs 淡水的差异表达。
Wald 检验
Wald 检验用于评估模型中某个系数(例如处理条件的效应)是否显著非零。在 RNA-seq 差异表达分析中,常用的负二项分布模型,对每个基因拟合模型:
$$ \log(\mu_{ij}) = \beta_0 + \beta_1 X_{condition} + \beta_2 X_{tissue} + \dots $$Wald 检验用来检验 $\beta_1$(处理条件效应)是否显著,适合样本量较小但模型拟合较稳定的场景。
Benjamini-Hochberg (BH) 校正
RNA-seq 数据通常包含成千上万个基因,每个基因都会产生一个 p 值。直接使用原始 p 值会导致大量假阳性(Type I error)。BH 方法控制假发现率 (FDR),即在所有被判定为显著的基因中,预期有多少比例是错误的。对于多比较问题(如 20,000 个基因),FDR 控制比 Bonferroni 更宽松、更合理,可以保留更多潜在的生物学信号。BH 校正对 p 值的分布无特殊假设,因此适合处理大量基因的多重检验问题,即使单个基因的样本量较小。
二、分析结果
2.1 差异表达基因概览
全局分析结果(控制组织效应)
| 指标 | 数值 |
|---|---|
| 总 DEG 数 | 422 |
| 上调基因(SEA > TAP) | 303 |
| 下调基因(SEA < TAP) | 119 |
| 上调/下调比 | 2.55 |
从整体差异表达分析结果来看,全局分析(控制组织效应)在16,866个有效基因中鉴定出422个差异表达基因,其中303个基因在海水环境中上调表达,119个基因下调,上调基因占比高达72%。这一结果表明,日本鳗鲡对海水盐度环境的响应主要表现为基因表达的激活而非抑制。上调/下调比达到2.55,说明海水环境触发了更为积极的基因表达程序,可能与渗透压调节、离子转运、能量代谢等适应机制密切相关。
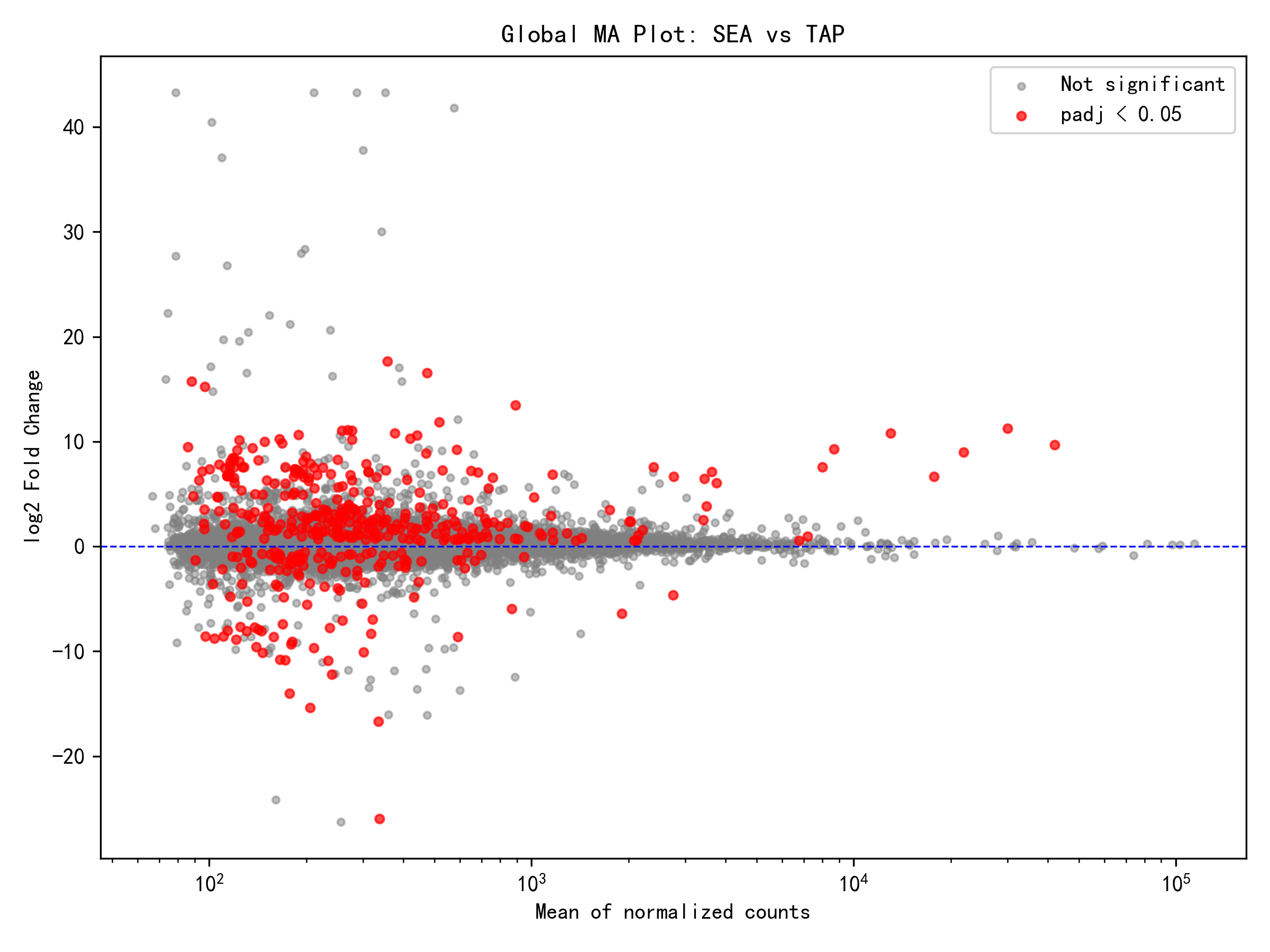
各组织单独分析结果
| 组织 | 总 DEG 数 | 上调 | 下调 | 上调/下调比 |
|---|---|---|---|---|
| 脑部(brain) | 500 | 340 | 160 | 2.13 |
| 性腺(gonad) | 131 | 75 | 56 | 1.34 |
| 胸鳍(pectoral_fins) | 97 | 82 | 15 | 5.47 |
在各组织的单独分析中,三个组织呈现出显著差异的响应模式。脑部组织检测到最多的差异表达基因(500个),其中340个上调、160个下调,上调/下调比为2.13,表明脑部对盐度变化最为敏感,这可能与神经内分泌调控渗透压适应反应的中枢功能相一致。性腺组织检测到131个差异表达基因,上调75个、下调56个,上调/下调比为1.34,是三个组织中比例最接近1:1的,提示性腺对盐度变化的响应相对平衡,可能涉及代谢和生殖功能的协调调整。胸鳍组织差异表达基因数量最少(97个),但上调/下调比高达5.47(82个上调、15个下调),显示出强烈的单向响应特征,暗示胸鳍中少数基因被海水环境强烈激活,可能编码与直接渗透压调节相关的功能蛋白。
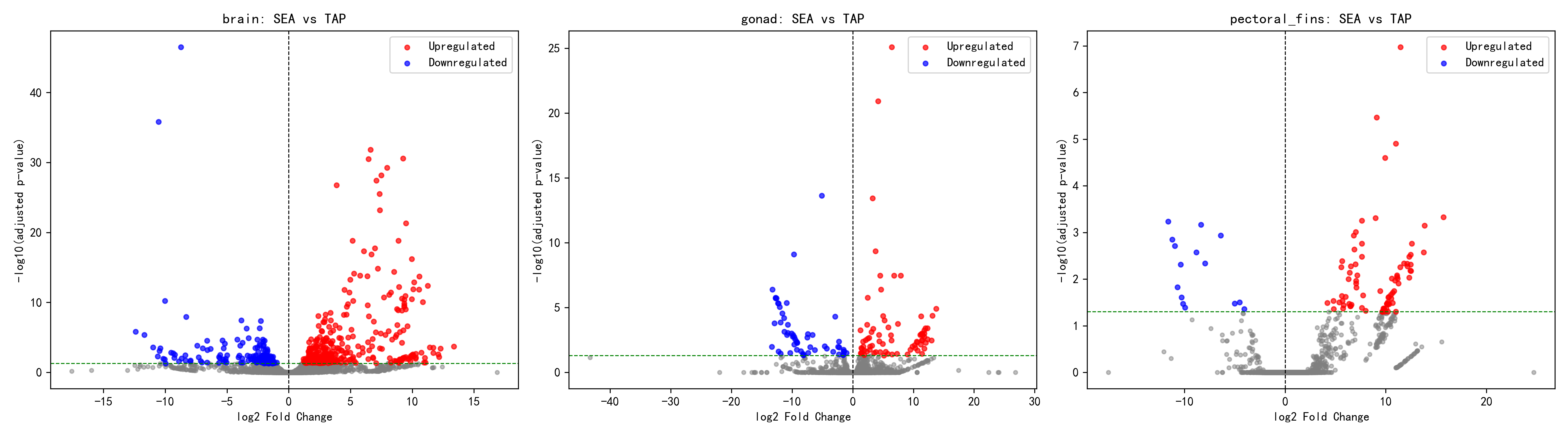
2.2 组织特异性响应分析
脑部(brain)——最敏感的盐度响应组织
脑部表现出最强的盐度响应,DEG 数量(500)远超其他组织。这一发现提示:
- 神经调控机制可能在盐度适应中起核心作用
- 脑部可能通过调节渗透压感受器和神经内分泌途径协调全身的盐度适应反应
- 高比例的上调基因(340/500 = 68%)表明海水环境激活了脑部广泛的基因表达程序
性腺(gonad)——中等强度的盐度响应
性腺的 DEG 数量(131)介于脑部和胸鳍之间,上调/下调比(1.34)也较为接近 1:1。这可能反映了:
- 繁殖器官对环境盐度变化有一定程度的响应
- 海水环境可能影响性腺的代谢和成熟过程
- 性别繁殖策略可能涉及对盐度的适应性调节
胸鳍(pectoral_fins)——保守的盐度响应
胸鳍的 DEG 数量最少(97),但上调/下调比最高(5.47),表明:
- 胸鳍对盐度变化的转录响应相对保守
- 少数基因在海水环境中被强烈激活
- 这些基因可能编码与盐度适应直接相关的蛋白质(如离子通道、渗透压调节蛋白)
2.3 核心响应基因(三组织共同显著)
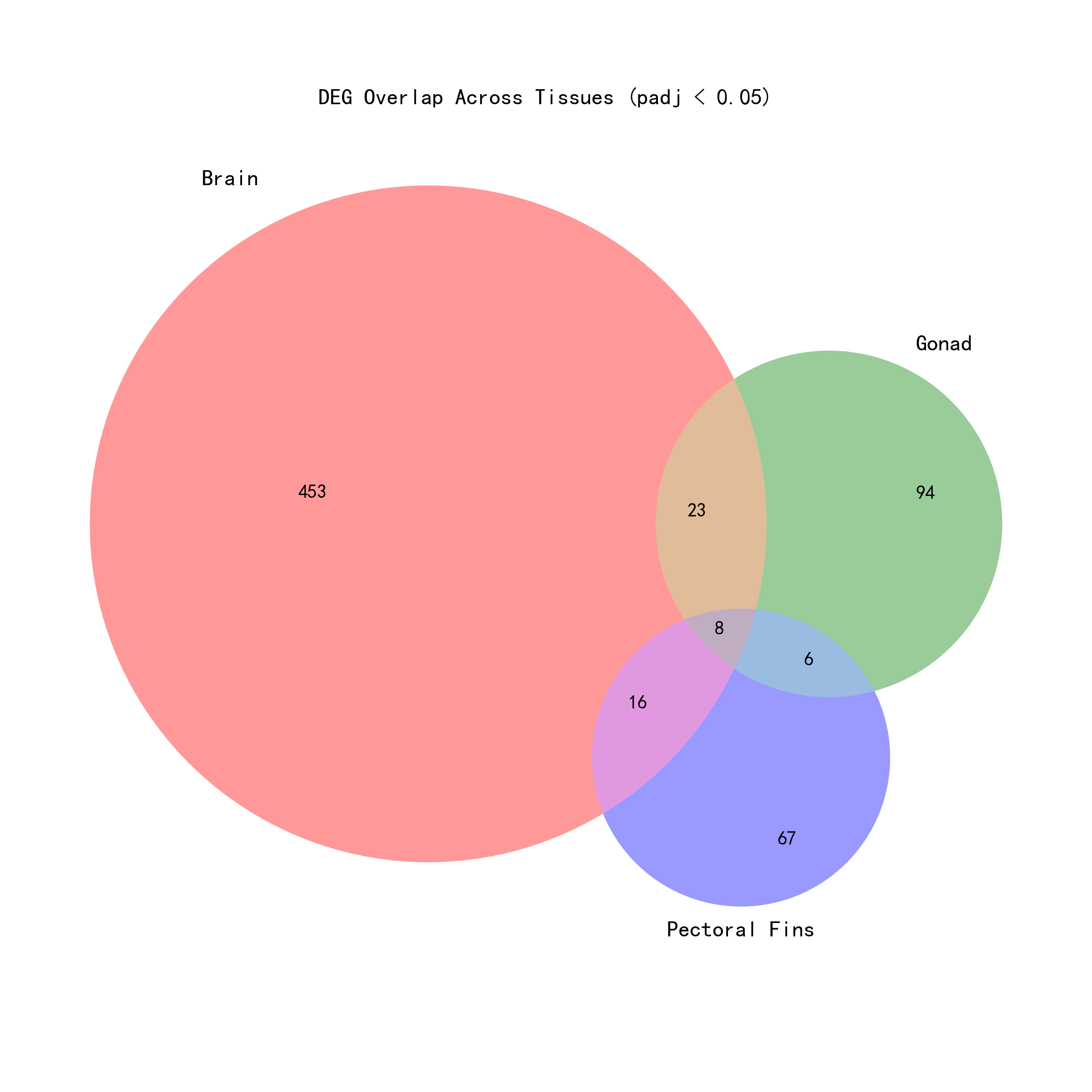
通过对三个组织单独分析结果取交集,鉴定出 8 个核心差异表达基因——这些基因在所有三个组织中均表现出显著的盐度响应(padj < 0.05):
| 基因 ID | 脑部 log2FC | 性腺 log2FC | 胸鳍 log2FC | 平均 log2FC |
|---|---|---|---|---|
| _TRINITY_DN215578_c8_g2_i4 | 11.41 | 10.20 | 11.25 | 10.95 |
| _TRINITY_DN212746_c1_g3_i1 | 8.36 | 11.78 | 9.63 | 9.92 |
| _TRINITY_DN196393_c2_g1_i4 | 7.71 | 4.68 | 12.12 | 8.17 |
| _TRINITY_DN210877_c3_g1_i17 | 8.97 | 4.37 | 11.16 | 8.17 |
| _TRINITY_DN192233_c0_g2_i2 | 7.38 | 4.51 | 12.58 | 8.16 |
| _TRINITY_DN193247_c3_g1_i5 | 9.49 | 3.52 | 7.74 | 6.92 |
| _TRINITY_DN220510_c3_g1_i1 | 9.28 | 4.17 | 5.66 | 6.37 |
| _TRINITY_DN192231_c4_g1_i1 | 5.60 | 5.45 | 6.01 | 5.69 |
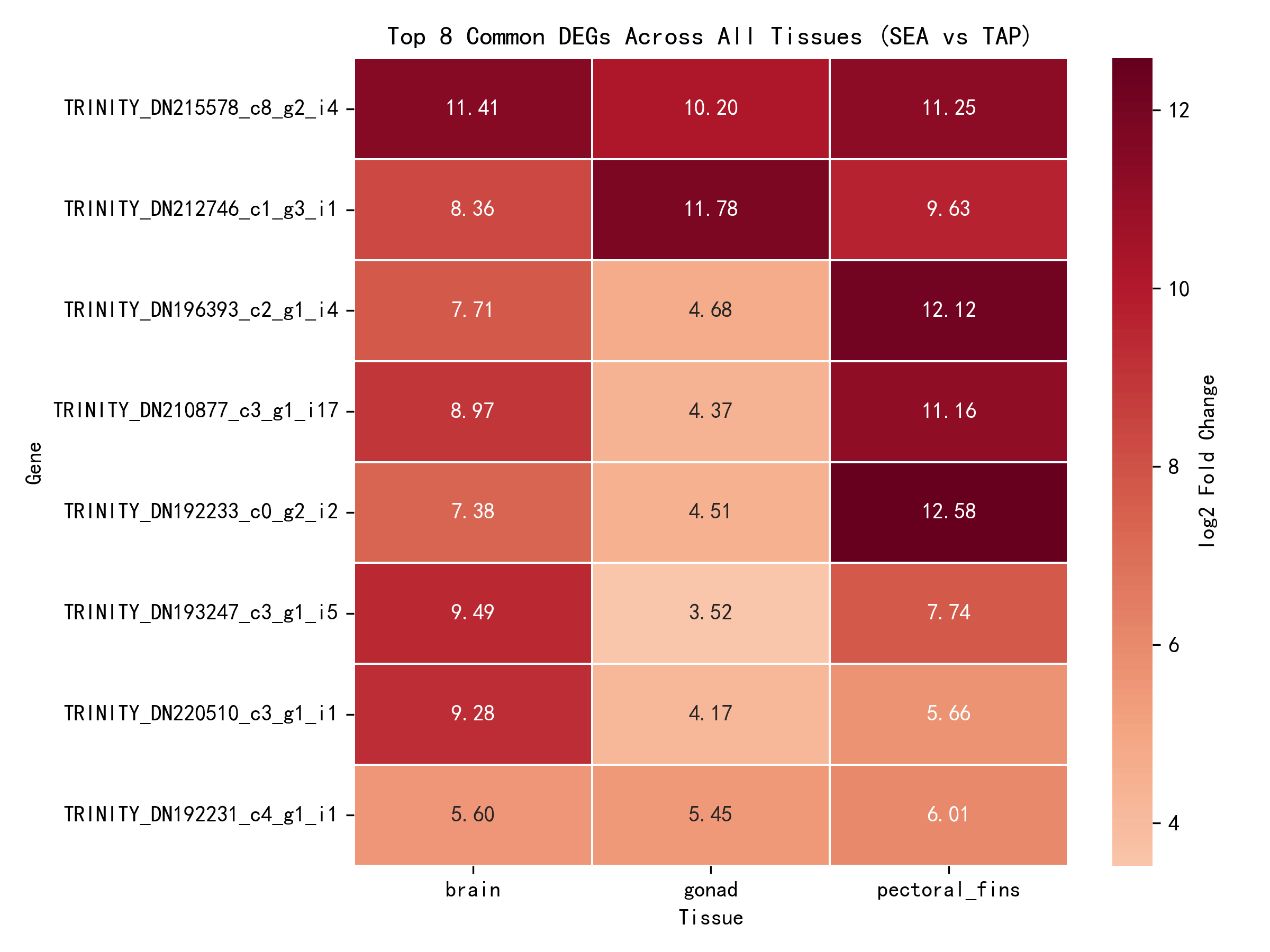
所有 8 个核心响应基因均呈现上调表达(log2FC > 0),表明这些基因在海水环境中表达增强,可能参与鳗鲡的盐度适应核心机制。
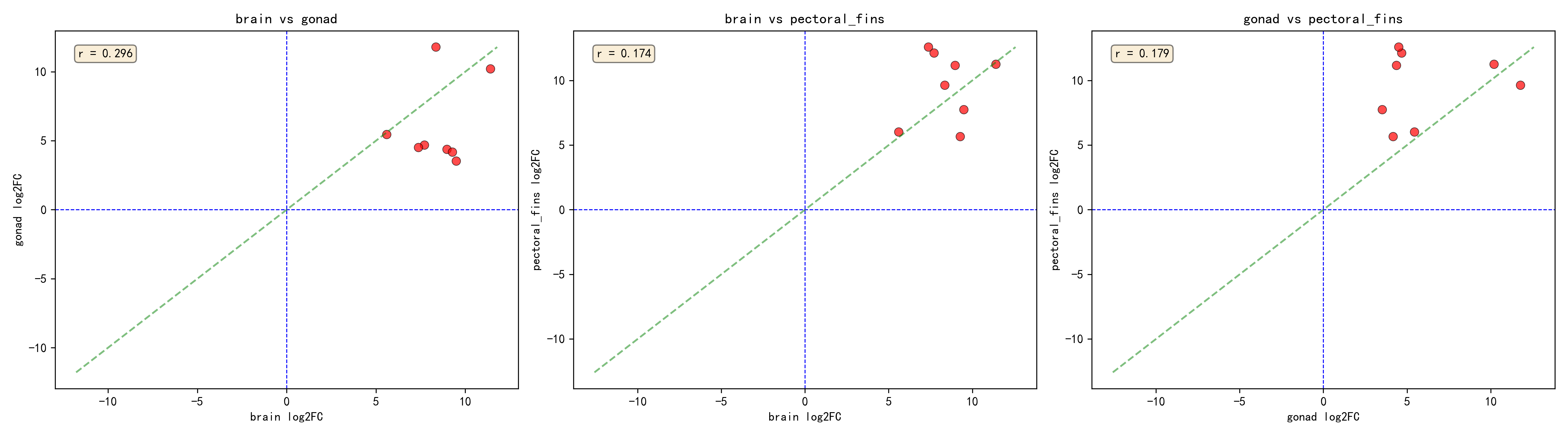
2.4 全局分析与单独分析的交叉验证
为全面理解两种分析策略的关系,对分析结果进行了交叉验证统计:
| 类别 | 基因数量 |
|---|---|
| 全局显著 (Global) | 422 |
| 三组织都显著 (Brain+Gonad+Pectoral_fins) | 8 |
| 三组织都显著,但全局不显著 | 0 |
| 全局显著,但不是三组织都显著 | 414 |
414个全局显著,但非三组织都显著的基因的进一步分类结果如下:
| 显著组织数 | 基因数 | 详情 |
|---|---|---|
| 0个组织显著 | 226 | 在各组织单独分析中都不显著 |
| 1个组织显著 | 148 | 104(仅脑部),31(仅性腺),13(仅胸鳍) |
| 2个组织显著 | 40 | 在两个组织中显著,但不是三个都显著 |
发现8个三组织都显著的基因在全局分析中也是显著的。存在大量全局显著,但不是三组织都显著的情况 — 共414个基因,占全局显著基因的98%(414/422)。特别值得关注的是那226个在单独组织分析中都不显著、但全局分析显著的基因 — 这类基因可能是因为全局分析通过跨组织整合提高了统计效能,能够检测到在单个组织中效应较弱但方向一致的基因。
三、结论与讨论
本研究采用全局分析与各组织单独分析相结合的策略,对海水与淡水环境下日本鳗鲡三个关键组织的差异表达基因进行了系统分析。全局分析控制组织效应鉴定出422个DEG,其中303个上调、119个下调;各组织单独分析显示脑部响应最强(500 DEG),性腺次之(131 DEG),胸鳍最保守(97 DEG)。通过交叉验证,发现8个在三组织中均显著上调的核心响应基因,以及226个仅在全局分析中显著、但在各组织单独分析中不显著的隐藏响应基因。
全局分析将组织作为协变量纳入模型,控制组织间基线差异后检测跨组织一致的处理效应,利用大样本量(n=15)获得较高的统计效能。各组织单独分析则在每个组织内独立检验,允许不同组织有不同的响应模式,通过三次独立校正和取交集获得更严格的结果。两种分析策略的交叉验证揭示了414个基因(占全局显著的98%)全局显著但非三组织都显著。其中,226个基因在各组织单独分析中均不显著,仅在全局分析中被检测到,这类基因的处理效应方向一致,但在单个组织中效应量较弱,全局分析通过跨组织整合提高了统计效能;148个基因仅在单个组织中显著(脑部104个、性腺31个、胸鳍13个);40个基因在两个组织中显著。典型情形是某个基因在脑组织中变化极强(如log2FC=4),在性腺和胸鳍中变化较弱(如log2FC=0.5),全局模型利用大样本量检测到显著效应,但单独分析时因样本量小(n=5)而不显著。
8个在三组织和全局分析中均显著一致的核心响应基因,其log2FC在所有组织中均大于5,表明这些基因对盐度变化的响应极其强烈。值得注意的是,本研究未出现三组织都显著但全局不显著的情况,这种情况较少见,但可能发生。例如:三个组织中效应方向相反(脑上调、性腺下调、胸鳍上调),而全局模型中这些效应会相互抵消。说明鳗鲡盐度适应中的组织特异性响应主要表现为效应量的差异,而非方向的对立。8个核心响应基因的处理效应不仅方向一致,而且在每个组织中效应都足够强,能够同时被两种分析策略检测到,代表了最稳健的盐度响应基因,值得进一步功能研究。
在所有单独分析显著的基因中,脑部特有的显著基因数量最多(104个),且脑部贡献了414个全局显著但非三组织都显著基因中的绝大部分。这与脑部作为渗透压感受器和神经内分泌调控中枢的功能相吻合,提示脑部在盐度感知和全身适应性响应调控中发挥主导作用。全局分析能够检测到在单个组织中效应较弱但方向一致的基因,这226个隐藏响应基因可能涉及基础的细胞渗透压调节机制,如普遍存在的离子通道、渗透压响应元件等,是盐度适应不可或缺的基础调控网络。
在盐度适应过程后,我们从日本鳗鲡的性腺组织中观察到,脂肪代谢相关基因的变化。TRINITY_DN187689_c0_g1_i9 的基因功能注释结果告诉我们,这一假定基因的后半段与金龙鱼(Scleropages formosus)Plin2(Perilipin 2)基因的多种transcript variant(转录剪接体)均存在相似的核苷酸序列,RNA表现量增加(pvalue = 0.0027,但校正后不显著 padj = 0.2023)。TRINITY_DN192327_c4_g3_i14则是金龙鱼编码鞘磷脂合酶1(Sphingomyelin synthase 1,Sgms1)相似的基因,在降海之后其RNA表现量下降。
Perilipin 2是一种脂肪分化相关蛋白,最初被命名为ADRP2,其转录水平的提高是脂肪细胞分化初期的迹象之一,但不是至关重要的,Plin2基因敲除以后脂肪的分化过程仍然可以正常进行3。可以确定的是Plin2与鞘磷脂(sphingomyelin, SM)和卵磷脂(phosphatidylcholine, PC)具有高度的亲和力4,但其功能尚不明确,似乎是为脂化的蛋白质提供了一个保护屏障,促进脂肪沉积,降低三油甘脂的周转5’6。
脂肪的合成、分化和沉积与日本鳗鲡性腺的发育密不可分。根据张洁明等对日本鳗鲡卵巢发育的分期和描述,在发育适应期,日本鳗鲡的卵母细胞开始出现一层或多层脂肪泡,进入发育启动期后脂肪泡厚度继续增加,排列更加紧密,到生长期厚度达到最大,之后开始减少松散7。日本鳗鲡开始洄游后,不再进食任何食物,身体能量和性腺的进一步发育都依赖于脂肪的利用,肌肉组织中的脂肪动员成为了卵巢发育的物质基础8。肌肉组织的磷脂代谢一般有三种不同的途径,包括:(1)溶酶体释放的磷脂酶消化;(2)肌肽酶水解形成鞘磷脂;(3)合成卵磷脂 9。我们猜想,降海过程日本鳗鲡Plin2 RNA表现量提高,Sgms1关闭,是因为脂肪经动员到达卵巢,既不被磷脂酶消化,也不合成鞘磷脂,而是在发育适应期开始沉积,为鱼卵所需的大量卵磷脂提供准备。
四、研究局限与展望
本研究存在以下局限:首先,样本量较小(SEA组3个,TAP组2个),统计效能受限,部分效应量中等的基因可能未能被检测到;其次,实验采用逐步升高的盐度驯化方式,与鳗鲡自然降海过程中经历的盐度变化可能存在差异;第三,本研究为转录组水平的分析,后续需要通过qPCR、Western blot等实验验证关键基因的表达变化,并通过功能实验(如基因敲除/过表达)阐明其在盐度适应中的具体作用。
此外,本研究鉴定出的8个核心响应基因已完成了系统的功能注释分析。这些基因在海水与淡水环境下表现出高度一致的表达响应模式,提示其可能参与鳗鲡盐度适应的核心调控通路,具有重要的生物学研究价值。然而,鉴于这些基因的调控网络解析工作尚在进行之中,相关成果尚未整理和公开发表,因此本论文仅呈现功能注释的初步结果。关于这些核心响应基因如何协同调控渗透压平衡、离子转运及能量代谢等关键生理过程,仍需进一步结合蛋白质互作组学、代谢组学及功能验证实验进行深入阐明。后续研究将重点解析这些基因在盐度适应过程中的上下游调控关系,以期构建日本鳗鲡盐度响应的完整调控网络,为理解鳗鲡洄游的分子机制提供理论依据。
-
郭弘艺, 魏凯, 谢正丽, 等. 长江口银色鳗的形态指标体系及其雌雄鉴别[J]. 水产学报, 2011, 35(1): 1-9. ↩︎
-
BRASAEMLE D L, BARBER T, WOLINS N E, et al. Adipose differentiation-related protein is an ubiquitously expressed lipid storage droplet-associated protein[J]. Journal of Lipid Research, 1997, 38(11):2249-2263. ↩︎
-
CHANG H J, LAN L, PAUL A, et al. Protection against Fatty Liver but Normal Adipogenesis in Mice Lacking Adipose Differentiation-Related Protein[J]. Molecular & Cellular Biology, 2006, 26(3):1063-1076. ↩︎
-
MCINTOSH A L, STOREY S M, ATSHAVES B P. Intracellular lipid droplets contain dynamic pools of sphingomyelin: ADRP binds phospholipids with high affinity[J]. Lipids, 2010, 45(6):465-477. ↩︎
-
LISTENBERGER L L, OSTERMEYER-FAY A G, GOLDBERG E B, et al. Adipocyte differentiation-related protein reduces the lipid droplet association of adipose triglyceride lipase and slows triacylglycerol turnover[J]. Journal of Lipid Research, 2007, 14(12):2751-2761. ↩︎
-
STRACKE F, MA H, THIEL E. Singlet molecular oxygen photosensitized by Rhodamine dyes: correlation with photophysical properties of the sensitizers[J]. Journal of Photochemistry & Photobiology A Chemistry, 1999, 126(1–3):51-58. ↩︎
-
张洁明, 柳凌, 郭峰, 等. 人工诱导日本鳗鲡性腺发育组织学研究[J]. 中国水产科学, 2007, 14(4): 593-601. ↩︎
-
张利红, 张为民, 林浩然, 等. 性类固醇激素诱导雌性日本鳗鲡性腺发育过程中钙和脂肪的动员[J]. 中山大学学报自然科学版, 2002, 40(2):86-88. ↩︎
-
SPENCE M W, CLARKE J T, COOK H W. Pathways of sphingomyelin metabolism in cultured fibroblasts from normal and sphingomyelin lipidosis subjects[J]. Journal of Biological Chemistry, 1983, 258(14):8595. ↩︎